A quantificação fotométrica por medidas de absorbância a 260 nm é amplamente utilizada para estimar rapidamente as concentrações de ácidos nucleicos antes de aplicações downstream. A concentração de ácidos nucléicos pode ser determinada a partir da lei de Lambert-Beer:

Onde:
c = (Equação 1) A εL onde:
A: absorbância medida a 260 nm (com subtração de absorbância de background a 320 nm)
L: caminho óptico (cm)
ε: coeficiente de extinção, ou absortividade intrínseca, de ácidos nucleicos, expresso em (µg/mL)–1(cm)–1
Para facilitar o uso da equação acima, muitas vezes é escrito como:

onde:
fator: corresponde a 1 / ε, expresso em (µg/mL).(cm)

Figura 1. Multiskan Sky conectado ao SkanIt Software 5.0
Para a estimativa de concentrações de dsDNA, DNA de fita simples (ssDNA) ou de RNA, são usados tipicamente os fatores – também chamados de “coeficientes padrão” por outros fabricantes – mostrados na Tabela 1. Esses fatores fornecem estimativas razoáveis para sequências longas de ácidos nucléicos com distribuição uniforme de bases, assumindo um caminho óptico de 1 cm.
Tabela 1. Fatores tipicamente utilizados para cálculos fotométricos de ácidos nucleicos, de acordo com a equação de Lambert-Beer.

Com o espectrofotômetro de microplacas Multiskan Sky as concentrações de ácidos nucleicos podem ser medidas usando várias plataformas de amostra, como a Thermo Scientific ™ μDrop ™ Plate, microplacas ou cubetas, cobrindo uma ampla gama de volumes A tabela 2 mostra as quantidades mínimas de amostra necessárias em cada plataforma.
Ao mudar as plataformas da amostra, um fator importante a ser considerado é o caminho óptico de luz. O caminho óptico é a distância pela qual a luz tem que passar para alcançar o detector. Quando uma amostra é medida em um espectrofotômetro padrão usando uma cubeta, a luz passa através da amostra horizontalmente e o caminho óptico de luz é fixo, normalmente a 1 cm. No entanto, quando são utilizados micro-volumes (na placa μDrop ou em microplacas), a luz passa pela amostra verticalmente e o caminho é mais curto e pode variar no caso das microplacas.

Figura 2. µDrop Plate recebendo amostras pela pipeta multicanal Finnpipette F1.
Nota: Recomendamos sempre realizar o cálculo das concentrações de dsDNA com subtração de background a 320 nm para excluir a interferência da dispersão de luz causada por partículas ou precipitados nas amostras.
As absorbâncias medidas de amostras e espaços em branco em microplacas são corrigidas em termos de comprimento de caminho óptico usando medições em 900 e 975 nm. O fator de correção é calculado usando a seguinte equação:
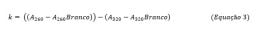
Onde:
A260 – A260Branco: absorbância medida a 260 nm para amostras e brancos, respectivamente (corrigidas para caminho óptico de 1 cm)
A320 – A320Branco: absorbância medida a 320 nm para amostras e brancos, respectivamente (corrigidas para caminho óptico de 1 cm)
Com essa técnica, seguindo as instruções descritas em nossos tutoriais, as concentrações de DNA bem como purezas podem ser facilmente calculadas usando o Multiskan Sky junto ao SkanIt Software 5.0 para qualquer plataforma. Além disso, modificações simples deste protocolo podem ser introduzidas para torná-lo aplicável para medições de RNA ou ssDNA.
Tabela 2. Diferentes formatos podem ser utilizados no Multiskan Sky para a quantificação de DNA.

Pureza
As razões de pureza são chave para indicar o sucesso da extração do DNA ou RNA, principalmente por acusar contaminações com proteínas e compostos fenólicos. A pureza determina o quão representativa é a leitura obtida a 260 nm em relação ao DNA presente naquela amostra (e, portanto, em relação ao valor calculado para a concentração de DNA). Uma absorbância alta a 260 nm pode na realidade vir de uma alta contaminação com proteínas, por exemplo.
O pH e a força iônica do diluente do NA afetam o valor encontrado na razão de pureza. Soluções ácidas tendem a gerar razões 0.2-0.3 unidades a menos. O mesmo funciona para soluções básicas, que geram razões 0.2-0.3 unidades a mais. É importante se assegurar de que as amostras e o branco estejam em um mesmo pH e força iônica.
Pureza 260/280
A razão entre absorbâncias medidas a 260 nm e 280 nm é a forma mais conhecida de controle de qualidade de uma extração de DNA ou RNA.
Falando de forma generalizada, o resultado da divisão expressa a proporção entre a quantidade de DNA e a quantidade de proteínas extraídos. Na prática, diversos métodos de extração utilizam compostos fenólicos, que acabam deixando resíduos e também absorvendo a 280 nm.
Os valores almejados são:
1.8: aceito como DNA “puro”
2.0: aceito como RNA “puro”
Pureza 260/230
Um pouco menos utilizada, ou menos conhecida, a razão 260/230 pode indicar contaminação com diversos compostos: fenóis, guanidina, beads magnéticas, carboidratos e proteínas.
Os valores almejados estão geralmente entre 1.8 e 2.2, um pouco acima de seus respectivos valores 260/280.
Varredura espectral
A varredura espectral geralmente é feita entre 220 e 350 nm, com resolução de 2 a 5 nm. Isso significa ter em mãos leituras de absorbância a cada 2 nm, por exemplo, desde 220 até 350 nm.
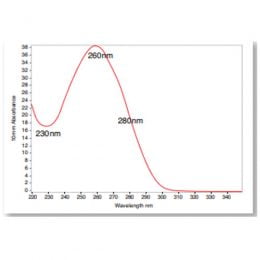
Figura 3. Espectro de absorbância esperado para leitura de DNA purificado de 220 a 350 nm
Nessa representação, os dados nos fornecem uma visão mais ampla da qualidade da extração. A contaminação química de amostras com baixas proporções de 260/280 pode frequentemente ser identificada através do exame da curva espectral. Conforme figura abaixo, as contaminações em 230 e 280 nm na verdade estão tornando o pico de absorbância do DNA erroneamente mais alto.
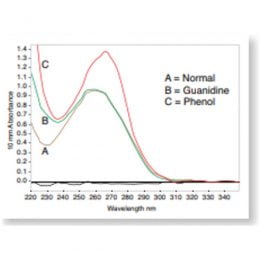
Figura 4. A alteração da curva espectral de absorbância do DNA purificado depende da natureza de seus contaminantes
Como cada contaminante possui seu perfil na varredura espectral, eles irão deformar a varredura esperada de formas diferentes. Veja abaixo o perfil espectral de alguns contaminantes.

Isotiocianato de Guanidina HCl Guanidina
Figura 5. Curvas espectrais de absorbância para contaminantes comuns do processo de extração de ácidos nucleicos.
Fatores que não podem ser inferidos pelas razões de pureza incluem o nível de degradação do AN e a contaminação por DNA exógeno. Essas características são, com frequência, verificadas em géis de eletroforese.
Dúvidas? Entre em contato!